TP3 - Analyse spectrale et modélisation
À rendre le 2026-04-12 - 14% du cours
- Contexte
- Objectifs
- Données
- Travail à faire
- Étape 1 - Lire les trois fichiers
- Étape 2 - Corriger les données
- Étape 3 - Isoler la résiduelle
- Étape 4 - Calculer les dérivées spatiales
- Étape 5 - Interpréter le piège
- Étape 6 - Construire un premier modèle du socle
- Étape 7 - Calculer la réponse gravimétrique du modèle
- Étape 8 - Ajuster le modèle
- Étape 9 - Calculer le volume
- Tutoriel
- Librairies
- Lecture des données
- Préparer les grilles
- Carte de couleur
- Corrections gravimétriques
- Fonction pour calculer l’anomalie régionale
- Dérivées spatiales
- Gravité d’un prisme rectangulaire
- Construire le modèle 3D du socle
- Comment faire l’« inversion » de façon simple
- Calculer la gravité du maillage de prismes
- Calcul du volume
- Références
Contexte
Le TP3 porte sur la caractérisation gravimétrique d’un site de stockage géologique du CO$_2$, inspiré de l’étude de Andrés et al. (2016). Vous disposerez d’un levé gravimétrique, de trois contraintes de forage et d’un maillage de prismes rectangulaires déjà défini. Votre travail consistera à :
- corriger les données gravimétriques,
- calculer l’anomalie de Bouguer,
- séparer la régionale et la résiduelle,
- utiliser les dérivées spatiales pour mieux délimiter la structure,
- construire un modèle 3D du socle à l’aide du maillage fourni,
- estimer le volume du piège.
Le maillage 3D étant déjà fourni, vous n’avez pas à chercher la position latérale de chaque prisme. La géométrie en plan des cellules est fixée. L’inconnue principale est donc la profondeur du socle, ou l’épaisseur du piège, dans chaque cellule active.
L’objectif du TP n’est pas de faire une inversion gravimétrique avancée, mais de construire un modèle géologiquement plausible, cohérent avec les forages, compatible avec les dérivées spatiales et capable de reproduire raisonnablement l’anomalie résiduelle observée.
Objectifs
Objectifs généraux
- Apprendre à filtrer des données géophysiques dans le domaine spectral.
- Comprendre l’utilité et les limites des différents filtres géophysiques.
- Relier une anomalie gravimétrique résiduelle à une géométrie 3D réaliste.
Objectifs spécifiques
- Corriger les données gravimétriques fournies et obtenir l’anomalie de Bouguer.
- Calculer l’anomalie régionale et l’anomalie résiduelle en effectuant un prolongement vers le haut de 100 m sur l’anomalie de Bouguer.
- Calculer des dérivées spatiales utiles à la délimitation du piège.
- Estimer la profondeur du socle dans un maillage 3D de prismes rectangulaires.
- Estimer le volume du piège géologique et valider cette estimation par modélisation gravimétrique 3D.
Données
Veuillez télécharger les fichiers suivants :
- TP3-GRAVITE-CO2.csv : levé gravimétrique.
- TP3-GRAVITE-CO2-WELLS.csv : contraintes de forage.
- TP3-GRAVITE-CO2-MESH.csv : maillage de modélisation 3D.
Toutes les données sont fournies dans les unités SI.
- Le levé contient 10 201 stations espacées de 20 m sur une grille uniforme carrée.
- La station de base est située aux coordonnées $(x, y)=(-1000, -1000)$.
- La correction de dérive a déjà été effectuée.
- Les corrections de latitude, d’altitude et de plateau n’ont pas été effectuées.
- Les trois forages interceptent le toit du piège à 50 m de profondeur.
- Le forage F1 est situé au centre d’une cellule du maillage aux coordonnées $(-208.33, 41.67)$ et confirme une épaisseur du piège de 75 m.
- Le forage F2 est situé au centre d’une cellule du maillage aux coordonnées $(125.00, -208.33)$ et confirme une épaisseur du piège de 100 m.
- Le forage F3 est situé au centre d’une cellule du maillage aux coordonnées $(41.67, 125.00)$ et confirme une épaisseur du piège de 125 m.
- Le maillage de modélisation contient 144 cellules (
12 x 12). - Certaines cellules sont inactives (
Active = 0) et ne doivent pas être utilisées dans le modèle. - La profondeur du toit du piège (
Top_depth_m) est imposée dans tout le maillage. - Le contraste de densité (
Density_contrast_kg_m3) est imposé et identique dans toutes les cellules. Sa valeur est de-450 kg/m^3.
La topographie et l’emplacement des forages sur le site sont montrés à la Figure 1.
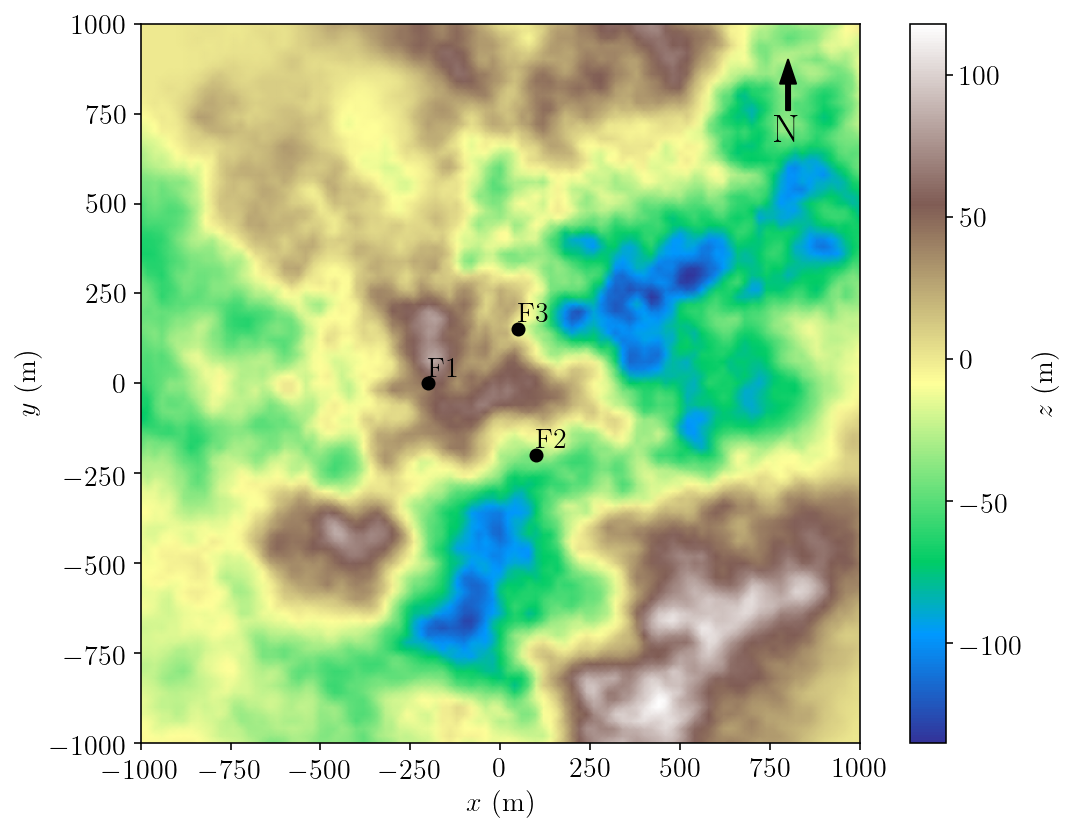
Figure 1. Carte topographique du site à l’étude.
La gravité observée sur le site est montrée à la Figure 2.
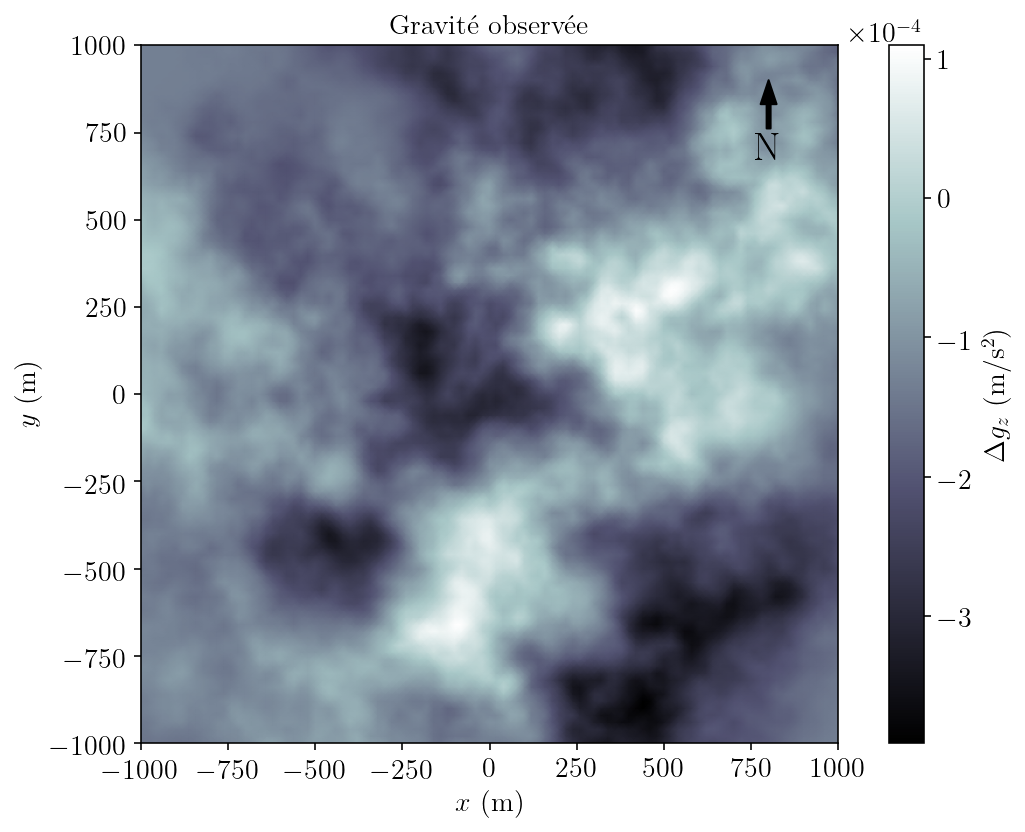
Figure 2. Carte de la gravité observée sur le site à l’étude.
Travail à faire
Le TP doit être traité comme un tutoriel guidé. Vous devez reproduire les étapes suivantes dans l’ordre.
Étape 1 - Lire les trois fichiers
Chargez les trois fichiers dans pandas, puis vérifiez :
- les colonnes disponibles,
- le nombre de lignes,
- les coordonnées minimales et maximales,
- le nombre de cellules actives du maillage.
À la fin de cette étape, vous devriez être capables de répondre aux questions suivantes :
- Combien y a-t-il de stations dans le levé ?
- Combien y a-t-il de cellules au total dans le maillage ?
- Combien de cellules sont actives ?
- Dans quelles cellules tombent les trois forages ?
Étape 2 - Corriger les données
À partir de g_obs_SI, calculez :
- la correction de latitude,
- la correction d’altitude,
- la correction de plateau,
- l’anomalie de Bouguer.
À cette étape, enregistrez au minimum les colonnes suivantes dans votre DataFrame :
corr_latcorr_altcorr_plaBouguer
La carte finale attendue pour cette étape ressemble à la Figure 3.
Figure 3. Carte de l’anomalie de Bouguer attendue après les corrections gravimétriques.
Étape 3 - Isoler la résiduelle
À partir de l’anomalie de Bouguer :
- calculez la régionale par prolongement vers le haut de 100 m,
- calculez la résiduelle par différence.
À cette étape, enregistrez au minimum :
RegionaleResiduelle
Vos cartes devraient ressembler qualitativement aux Figure 4 et Figure 5.
Figure 4. Exemple d’anomalie régionale obtenue par prolongement vers le haut de 100 m.
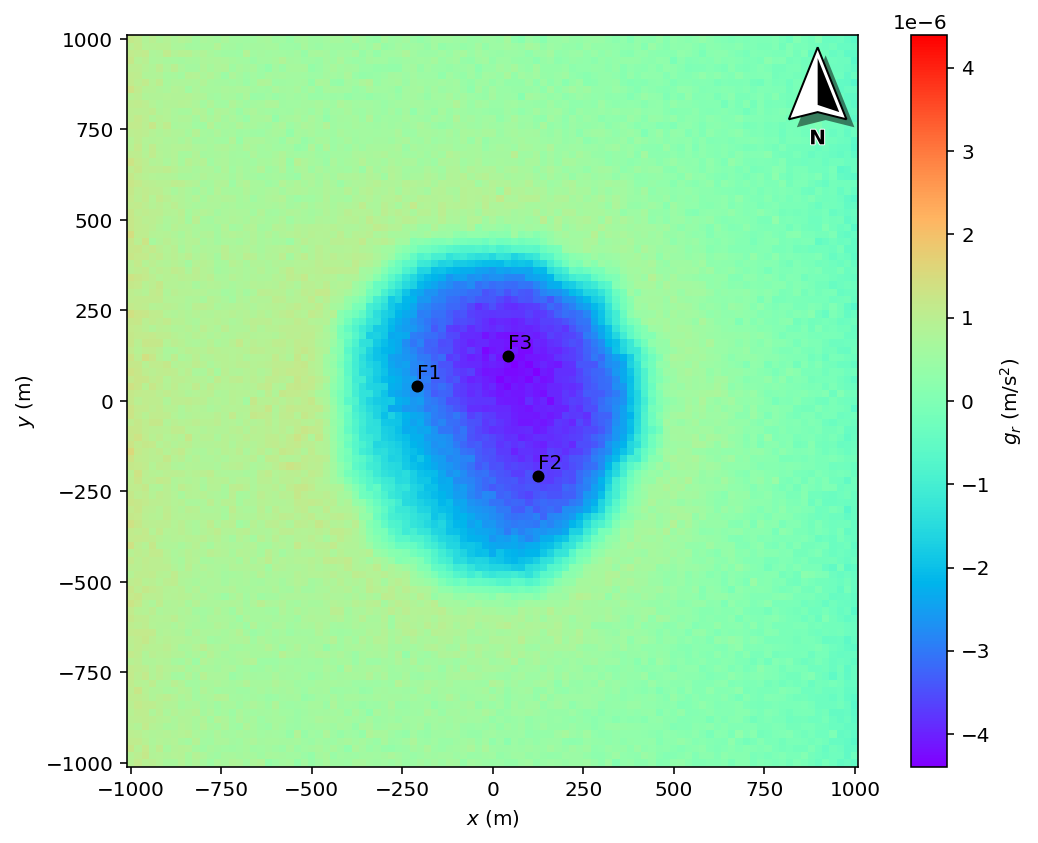
Figure 5. Exemple d’anomalie résiduelle obtenue par soustraction de la régionale.
Étape 4 - Calculer les dérivées spatiales
À partir de l’anomalie résiduelle, calculez :
- $\partial g / \partial x$,
- $\partial g / \partial y$,
- $\partial g / \partial z$,
- $\partial^2 g / \partial z^2$,
- le signal analytique.
À cette étape, enregistrez au minimum :
ddxddyddzddz2SA
La Figure 6 montre un exemple de signal analytique qui peut vous aider à valider cette étape.
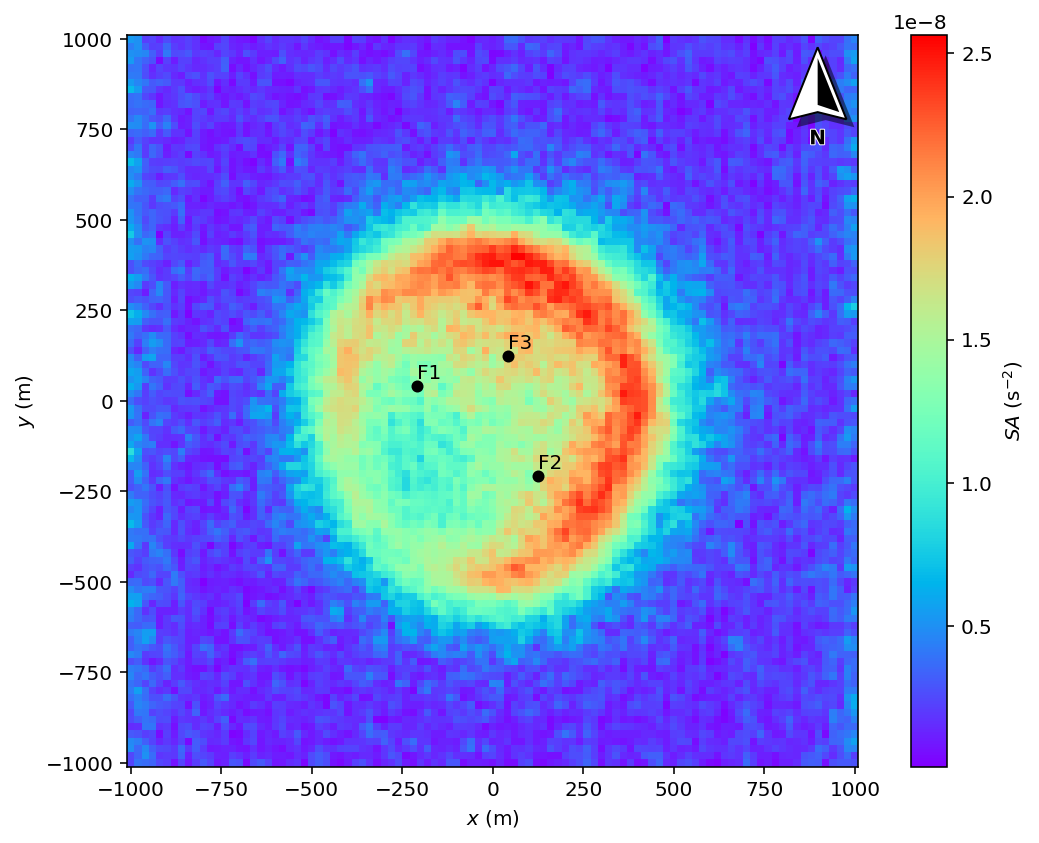
Figure 6. Exemple de signal analytique calculé à partir de l’anomalie résiduelle.
Étape 5 - Interpréter le piège
À partir de la résiduelle et des dérivées :
- délimitez la zone du piège,
- vérifiez la cohérence avec la position des trois forages,
- identifiez quelles cellules actives du maillage doivent contenir le piège.
Concrètement, à la fin de cette étape, vous devriez avoir :
- une idée de la forme générale du piège;
- une idée de son extension latérale;
- une hypothèse géologique raisonnable sur les cellules les plus épaisses.
Étape 6 - Construire un premier modèle du socle
Attribuez une épaisseur à chaque cellule active :
- imposez les épaisseurs connues dans les cellules des forages,
- proposez une interpolation ou une distribution plausible pour les autres cellules,
- convertissez cette épaisseur en profondeur du socle.
Le but de cette étape est d’obtenir un modèle initial, pas un modèle parfait. Ce premier modèle doit surtout :
- être lisse;
- respecter exactement les trois forages, mais de façon lissée dans l’espace;
- rester compatible avec la forme de l’anomalie résiduelle.
Votre carte finale du socle devrait avoir une allure comparable à la Figure 7.
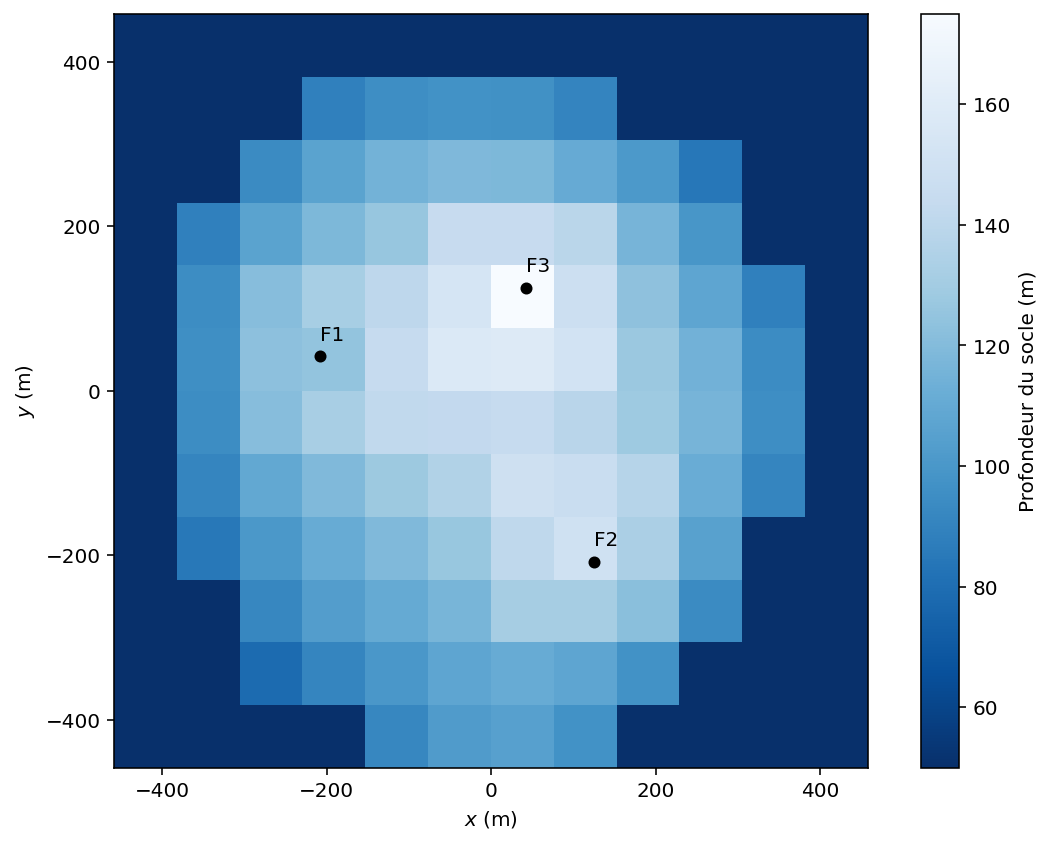
Figure 7. Exemple de carte finale de profondeur du socle obtenue à partir du modèle 3D.
Étape 7 - Calculer la réponse gravimétrique du modèle
Calculez la réponse gravimétrique du maillage de prismes.
Le modèle de prismes représente déjà la source locale, mais l’anomalie résiduelle observée est un champ filtré. Pour comparer correctement le modèle et les données, vous devez donc appliquer au modèle le même traitement spectral qu’aux données. Autrement dit, la comparaison doit se faire entre deux quantités traitées de la même manière :
- la résiduelle observée obtenue à partir de la Bouguer,
- la résiduelle modélisée obtenue à partir de la gravité du maillage de prismes.
À la fin de cette étape, vous devez avoir :
- une carte de la gravité modélisée;
- une carte de la résiduelle modélisée;
- une carte ou une mesure numérique du misfit.
Étape 8 - Ajuster le modèle
Ajustez les profondeurs du socle jusqu’à obtenir :
- une géométrie plausible,
- un accord raisonnable entre résiduelle observée et résiduelle modélisée,
- un modèle compatible avec les forages.
Dans ce TP, l’« inversion » attendue doit être simple et explicite. Vous n’avez pas à coder une méthode d’optimisation avancée. La stratégie recommandée est la suivante :
- construire un modèle initial du socle à partir des trois forages;
- calculer la résiduelle modélisée de ce modèle initial;
- effectuer une recherche exhaustive sur un facteur d’échelle global appliqué aux épaisseurs;
- conserver le facteur qui minimise le misfit quadratique moyen entre résiduelle observée et résiduelle modélisée;
- vérifier que les cellules des forages restent compatibles avec les contraintes géologiques;
- produire la carte finale du socle et le volume.
Autrement dit, on vous demande ici une inversion très simple à un paramètre, appuyée sur un modèle initial géologiquement plausible.
Le point important est le suivant : vous ne devez pas tester des profondeurs complètement aléatoires cellule par cellule. La procédure attendue est :
- construire une géométrie initiale plausible;
- conserver cette géométrie générale;
- ajuster son amplitude globale par recherche exhaustive;
- choisir le meilleur facteur avec un critère quantitatif, par exemple le RMSE.
Étape 9 - Calculer le volume
Calculez le volume total du piège à partir des épaisseurs finales.
Tutoriel
Librairies
import numpy as np
import pandas as pd
import matplotlib.pyplot as plt
Vous pouvez aussi utiliser pathlib :
from pathlib import Path
root = Path(".")
df = pd.read_csv(root / "TP3-GRAVITE-CO2.csv")
wells = pd.read_csv(root / "TP3-GRAVITE-CO2-WELLS.csv")
mesh = pd.read_csv(root / "TP3-GRAVITE-CO2-MESH.csv")
Lecture des données
df = pd.read_csv("TP3-GRAVITE-CO2.csv") # leve gravimetrique
wells = pd.read_csv("TP3-GRAVITE-CO2-WELLS.csv") # contraintes de forage
mesh = pd.read_csv("TP3-GRAVITE-CO2-MESH.csv") # maillage de modelisation
print(df.head()) # apercu du leve
print(wells) # tableau des forages
print(mesh.head()) # apercu du maillage
Colonnes utiles :
- Dans
df:X,Y,Z,g_obs_SI - Dans
wells:Well,X,Y,Trap_top_m,Trap_thickness_m,Socle_depth_m - Dans
mesh:Cell_ID,X1,X2,Y1,Y2,X_center,Y_center,Active,Top_depth_m,Density_contrast_kg_m3
Préparer les grilles
Avant de faire des cartes ou des filtres, remettez les données en grille.
nx = df["X"].nunique() # nombre de colonnes
ny = df["Y"].nunique() # nombre de lignes
xx = df["X"].values.reshape(ny, nx) # grille X
yy = df["Y"].values.reshape(ny, nx) # grille Y
zz = df["Z"].values.reshape(ny, nx) # grille topographique
gobs = df["g_obs_SI"].values.reshape(ny, nx) # grille de gravite observee
Carte de couleur
Utilisez les conventions suivantes :
rainbowpour les cartes gravimétriques,terrainpour la topographie,Blues_rpour la profondeur du socle.
Exemple :
plt.figure(figsize=(8, 6)) # taille de la figure
plt.pcolormesh(xx, yy, gobs, cmap="rainbow") # carte coloree
plt.gca().set_aspect("equal") # meme echelle en x et y
plt.colorbar(label="$g_z$ (m/s$^2$)") # barre de couleurs
plt.xlabel("$x$ (m)") # axe x
plt.ylabel("$y$ (m)") # axe y
Corrections gravimétriques
Les constantes à utiliser sont :
G = 6.6743e-11 # constante gravitationnelle
rho_plateau = 2400 # densite du plateau de Bouguer
grad_alt = 3.083e-6 # gradient de l'air libre
g_e = 9.7803267715 # gravite normale a l'equateur
c1 = 5.2790414e-3 # coefficient de la correction de latitude
R_e = 6.378e6 # rayon equatorial de la Terre
lat_hontomin_deg = 42.5716 # latitude de Hontomin
Calcul :
z0 = df["Z"].iloc[0] # altitude de reference
y0 = df["Y"].iloc[0] # coordonnee y de reference
lat0 = np.radians(lat_hontomin_deg) # latitude de Hontomin en radians
df["corr_lat"] = -(g_e * c1 * np.sin(2 * lat0) / R_e) * (df["Y"] - y0) # correction de latitude
df["corr_alt"] = -grad_alt * (df["Z"] - z0) # correction d'altitude
df["corr_pla"] = 2 * np.pi * G * rho_plateau * (df["Z"] - z0) # correction de plateau
df["Bouguer"] = (
df["g_obs_SI"] # gravite observee
+ grad_alt * (df["Z"] - z0) # retrait de l'altitude
- 2 * np.pi * G * rho_plateau * (df["Z"] - z0) # retrait du plateau
+ (g_e * c1 * np.sin(2 * lat0) / R_e) * (df["Y"] - y0) # retrait de la latitude
) # anomalie de Bouguer
Ici, utilisez explicitement la formule du cours $\Delta g_\mathrm{L} = -\dfrac{g_\mathrm{e} c_1 \sin(2\phi)}{R_\mathrm{e}} (y - y_0)$ avec la latitude de Hontomín.
Fonction pour calculer l’anomalie régionale
def calcul_regionale(x, y, gz, h):
nx = x.nunique() # taille en x
ny = y.nunique() # taille en y
grille = gz.values.reshape(ny, nx) # remise en grille
grille_pad = np.pad(grille, ((ny, ny), (nx, nx)), mode="reflect") # ajout d'une bordure
gz_hat = np.fft.fft2(grille_pad) # transformee de Fourier
dx = x.diff().dropna().max() # pas en x
dy = y.diff().dropna().max() # pas en y
kx = 2 * np.pi * np.fft.fftfreq(3 * nx, d=dx) # nombres d'onde en x
ky = 2 * np.pi * np.fft.fftfreq(3 * ny, d=dy) # nombres d'onde en y
KXX, KYY = np.meshgrid(kx, ky) # grille spectrale
filtre = np.exp(-h * np.sqrt(KXX**2 + KYY**2)) # filtre de prolongement vers le haut
regionale_pad = np.fft.ifft2(gz_hat * filtre).real # retour dans l'espace
regionale = regionale_pad[ny:-ny, nx:-nx] # retrait de la bordure
return regionale.flatten() # retour en vecteur
Utilisation :
df["Regionale"] = calcul_regionale(df["X"], df["Y"], df["Bouguer"], h=100) # champ regional
df["Residuelle"] = df["Bouguer"] - df["Regionale"] # champ local
Dans ce TP, la hauteur de prolongement demandée est 100 m.
Dérivées spatiales
Exemple de dérivée verticale :
def derivee_verticale(x, y, gz, ordre=1):
nx = x.nunique() # taille en x
ny = y.nunique() # taille en y
grille = gz.values.reshape(ny, nx) # remise en grille
grille_pad = np.pad(grille, ((ny, ny), (nx, nx)), mode="reflect") # ajout d'une bordure
gz_hat = np.fft.fft2(grille_pad) # transformee de Fourier
dx = x.diff().dropna().max() # pas en x
dy = y.diff().dropna().max() # pas en y
kx = 2 * np.pi * np.fft.fftfreq(3 * nx, d=dx) # nombres d'onde en x
ky = 2 * np.pi * np.fft.fftfreq(3 * ny, d=dy) # nombres d'onde en y
KXX, KYY = np.meshgrid(kx, ky) # grille spectrale
filtre = np.sqrt(KXX**2 + KYY**2) ** ordre # filtre de derivee verticale
derivee_pad = np.fft.ifft2(gz_hat * filtre).real # retour dans l'espace
derivee = derivee_pad[ny:-ny, nx:-nx] # retrait de la bordure
return derivee.flatten() # retour en vecteur
Exemple de dérivées horizontales :
def derivees_horizontales(x, y, gz):
nx = x.nunique() # taille en x
ny = y.nunique() # taille en y
grille = gz.values.reshape(ny, nx) # remise en grille
grille_pad = np.pad(grille, ((ny, ny), (nx, nx)), mode="reflect") # ajout d'une bordure
gz_hat = np.fft.fft2(grille_pad) # transformee de Fourier
dx = x.diff().dropna().max() # pas en x
dy = y.diff().dropna().max() # pas en y
kx = 2 * np.pi * np.fft.fftfreq(3 * nx, d=dx) # nombres d'onde en x
ky = 2 * np.pi * np.fft.fftfreq(3 * ny, d=dy) # nombres d'onde en y
KXX, KYY = np.meshgrid(kx, ky) # grille spectrale
ddx_pad = np.fft.ifft2(gz_hat * (1j * KXX)).real # derivee selon x
ddy_pad = np.fft.ifft2(gz_hat * (1j * KYY)).real # derivee selon y
ddx = ddx_pad[ny:-ny, nx:-nx] # retrait de la bordure
ddy = ddy_pad[ny:-ny, nx:-nx] # retrait de la bordure
return ddx.flatten(), ddy.flatten() # retour en vecteurs
Puis :
df["ddz"] = derivee_verticale(df["X"], df["Y"], df["Residuelle"], ordre=1) # 1re derivee verticale
df["ddz2"] = derivee_verticale(df["X"], df["Y"], df["Residuelle"], ordre=2) # 2e derivee verticale
df["ddx"], df["ddy"] = derivees_horizontales(df["X"], df["Y"], df["Residuelle"]) # derivees horizontales
df["SA"] = np.sqrt(df["ddx"]**2 + df["ddy"]**2 + df["ddz"]**2) # signal analytique
Remarque importante :
- Les dérivées servent surtout à interpréter la géométrie du piège.
- Elles ne servent pas directement à calculer les profondeurs cellule par cellule.
- Le signal analytique est particulièrement utile pour visualiser les limites du corps.
Gravité d’un prisme rectangulaire
La composante verticale de la gravité mesurée aux coordonnées d’observation $x, y, z$ et causée par un prisme rectangulaire de contraste de densité $\Delta\rho$ dont les côtés sont aux coordonnées $x_i, y_j, z_k$ est (Li & Chouteau, 1998)
\(\Delta g_z = G \Delta\rho \sum_{i=1}^2 \sum_{j=1}^2 \sum_{k=1}^2 \mu_{ijk} \left[ \Delta x_i \ln{}(\Delta y_j + r_{ijk}) + \Delta y_j \ln{}(\Delta x_i + r_{ijk}) - \Delta z_k \arctan{\frac{\Delta x_i \Delta y_j}{\Delta z_k r_{ijk}}} \right]\),
où $G$ est la constante gravitationnelle,
$ \Delta x_i = x - x_i $,
$ \Delta y_j = y - y_j $,
$ \Delta z_k = z - z_k $,
$ r_{ijk} = \sqrt{\Delta x_i^2 + \Delta y_j^2 + \Delta z_k^2} $
et
$ \mu_{ijk} = (-1)^i (-1)^j (-1)^k $.
Gabarit Python :
def calculer_g_prisme(rho, x12, y12, z12, x, y, z):
G = 6.6743e-11 # constante gravitationnelle
gz = np.zeros_like(x, dtype=float) # accumulation de la gravite
for i in range(2):
for j in range(2):
for k in range(2):
dx = x - x12[i] # distance en x
dy = y - y12[j] # distance en y
dz = z - z12[k] # distance en z
r = np.sqrt(dx**2 + dy**2 + dz**2) # distance totale
mu = (-1)**i * (-1)**j * (-1)**k # signe du coin
gz += mu * (
dx * np.log(dy + r) # terme logarithmique 1
+ dy * np.log(dx + r) # terme logarithmique 2
- dz * np.arctan2(dx * dy, dz * r) # terme arctangente
)
return -G * rho * gz # gravite verticale du prisme
Construire le modèle 3D du socle
Le maillage fixe la géométrie latérale. Il vous reste à attribuer une épaisseur à chaque cellule active.
Commencez par :
- garder les cellules actives;
- créer une colonne d’épaisseur;
- construire une première interpolation lisse à partir des trois forages;
- imposer ensuite les forages par une correction gaussienne locale, plutôt qu’en remplaçant brutalement une seule cellule.
Exemple :
mesh_actif = mesh[mesh["Active"] == 1].copy() # garder seulement les cellules actives
mesh_actif["Epaisseur_m"] = 0.0 # initialiser les epaisseurs
Ensuite, vous devez attribuer les autres épaisseurs. Une manière simple de démarrer consiste à interpoler depuis les forages :
for i, cellule in mesh_actif.iterrows():
dx = wells["X"] - cellule["X_center"] # distance aux forages en x
dy = wells["Y"] - cellule["Y_center"] # distance aux forages en y
distance2 = dx**2 + dy**2 # distance au carre
poids = np.exp(-distance2 / (2 * 220.0**2)) # poids gaussien
mesh_actif.loc[i, "Epaisseur_m"] = np.sum(poids * wells["Trap_thickness_m"]) / np.sum(poids) # moyenne ponderee
Pour respecter exactement les forages sans créer de pics trop brusques, appliquez ensuite une correction locale lissée :
def imposer_forages_en_douceur(mesh_modele, wells, sigma=150.0):
mesh_modele = mesh_modele.copy()
for _, well in wells.iterrows():
masque = (
np.isclose(mesh_modele["X_center"], well["X"])
& np.isclose(mesh_modele["Y_center"], well["Y"])
)
epaisseur_actuelle = mesh_modele.loc[masque, "Epaisseur_m"].iloc[0]
correction = well["Trap_thickness_m"] - epaisseur_actuelle
dx = mesh_modele["X_center"] - well["X"]
dy = mesh_modele["Y_center"] - well["Y"]
distance2 = dx**2 + dy**2
poids = np.exp(-distance2 / (2 * sigma**2))
poids = poids / poids[masque].iloc[0]
mesh_modele["Epaisseur_m"] += correction * poids
return mesh_modele
mesh_actif = imposer_forages_en_douceur(mesh_actif, wells, sigma=150.0)
Ce n’est qu’un point de départ. Vous devrez ensuite ajuster le modèle en fonction :
- de la position de l’anomalie résiduelle,
- du signal analytique,
- des dérivées spatiales,
- de la géométrie plausible du piège.
Comment faire l’« inversion » de façon simple
Voici la procédure attendue pour ajuster votre modèle.
1. Construire un modèle initial
Le modèle initial doit :
- respecter exactement les trois forages;
- donner des épaisseurs nulles dans les cellules inactives;
- être lisse et plausible dans les cellules actives.
2. Calculer la résiduelle modélisée du modèle initial
Calculez d’abord la gravité du maillage, puis appliquez le même prolongement vers le haut de 100 m qu’aux données pour obtenir une résiduelle modélisée comparable :
gz_modele = np.zeros(len(df)) # gravite totale du modele
for _, cellule in mesh_actif.iterrows():
epaisseur = cellule["Epaisseur_m"] # epaisseur de la cellule
if epaisseur <= 0: # ignorer les cellules sans piege
continue
x12 = [cellule["X1"], cellule["X2"]] # limites en x
y12 = [cellule["Y1"], cellule["Y2"]] # limites en y
z12 = [-(cellule["Top_depth_m"] + epaisseur), -cellule["Top_depth_m"]] # base et toit du prisme
gz_modele += calculer_g_prisme(
cellule["Density_contrast_kg_m3"], # contraste de densite
x12, # limites x
y12, # limites y
z12, # limites z
df["X"].values, # points d'observation x
df["Y"].values, # points d'observation y
np.zeros(len(df)), # points d'observation z
)
gz_modele_series = pd.Series(gz_modele) # conversion en serie pandas
regionale_modele = calcul_regionale(df["X"], df["Y"], gz_modele_series, h=100) # meme filtrage que les donnees
residuelle_modele = gz_modele - regionale_modele # champ local modele
3. Faire une recherche exhaustive sur un facteur d’échelle
L’idée est de garder la forme générale du modèle initial, mais de tester plusieurs amplitudes globales :
facteurs = np.linspace(0.2, 2.0, 181) # facteurs testes
meilleur_facteur = None # meilleur facteur trouve
meilleure_erreur = np.inf # meilleure erreur trouvee
for facteur in facteurs:
mesh_test = mesh_actif.copy() # copie du modele initial
mesh_test["Epaisseur_m"] = facteur * mesh_actif["Epaisseur_m"] # mise a l'echelle globale
mesh_test = imposer_forages_en_douceur(mesh_test, wells, sigma=150.0) # forages imposes en douceur
gz_test = np.zeros(len(df)) # gravite du modele teste
for _, cellule in mesh_test.iterrows():
epaisseur = cellule["Epaisseur_m"] # epaisseur testee
if epaisseur <= 0: # ignorer les cellules vides
continue
x12 = [cellule["X1"], cellule["X2"]] # limites x
y12 = [cellule["Y1"], cellule["Y2"]] # limites y
z12 = [-(cellule["Top_depth_m"] + epaisseur), -cellule["Top_depth_m"]] # limites z
gz_test += calculer_g_prisme(
cellule["Density_contrast_kg_m3"],
x12,
y12,
z12,
df["X"].values,
df["Y"].values,
np.zeros(len(df)),
)
residuelle_test = gz_test - calcul_regionale(df["X"], df["Y"], pd.Series(gz_test), h=100) # residuelle du modele
erreur = np.sqrt(np.mean((df["Residuelle"].values - residuelle_test) ** 2)) # RMSE
if erreur < meilleure_erreur:
meilleure_erreur = erreur # mise a jour de la meilleure erreur
meilleur_facteur = facteur # mise a jour du meilleur facteur
print(meilleur_facteur, meilleure_erreur) # facteur retenu et RMSE
Interprétation :
- si
facteur < 1, votre modèle initial était globalement trop épais; - si
facteur > 1, votre modèle initial était globalement trop mince.
4. Construire le modèle final
Une fois le meilleur facteur trouvé :
mesh_final = mesh_actif.copy() # copie du modele initial
mesh_final["Epaisseur_m"] = meilleur_facteur * mesh_actif["Epaisseur_m"] # appliquer le meilleur facteur
mesh_final = imposer_forages_en_douceur(mesh_final, wells, sigma=150.0) # forages imposes en douceur
mesh_final["Socle_m"] = mesh_final["Top_depth_m"] + mesh_final["Epaisseur_m"] # profondeur finale du socle
5. Vérifier le résultat
Le but n’est pas d’obtenir un misfit nul, mais un modèle cohérent et défendable. Pour vous guider, posez-vous ces questions :
- Les plus fortes épaisseurs sont-elles situées dans une zone cohérente avec les forages ?
- Le socle varie-t-il de manière relativement lisse ?
- Le modèle final reproduit-il la géométrie principale de la résiduelle ?
- Le volume final est-il raisonnable compte tenu de l’étendue du piège ?
Calculer la gravité du maillage de prismes
gz_modele = np.zeros(len(df)) # gravite totale du maillage
for _, cellule in mesh_actif.iterrows():
epaisseur = cellule["Epaisseur_m"] # epaisseur locale
if epaisseur <= 0: # ignorer les cellules sans piege
continue
x12 = [cellule["X1"], cellule["X2"]] # limites x
y12 = [cellule["Y1"], cellule["Y2"]] # limites y
z12 = [-(cellule["Top_depth_m"] + epaisseur), -cellule["Top_depth_m"]] # limites z
gz_modele += calculer_g_prisme(
cellule["Density_contrast_kg_m3"],
x12,
y12,
z12,
df["X"].values,
df["Y"].values,
np.zeros(len(df)),
)
Comme l’anomalie résiduelle observée est filtrée, il faut appliquer exactement le même traitement spectral au modèle :
gz_modele_series = pd.Series(gz_modele) # conversion en serie
regionale_modele = calcul_regionale(df["X"], df["Y"], gz_modele_series, h=100) # meme filtrage
residuelle_modele = gz_modele - regionale_modele # residuelle modelee
Le misfit peut ensuite être calculé :
erreur = df["Residuelle"].values - residuelle_modele # ecart point par point
rmse = np.sqrt(np.mean(erreur**2)) # erreur quadratique moyenne
print(rmse) # valeur du misfit
Vous pouvez aussi enregistrer l’erreur pour chaque facteur testé dans une liste et tracer la courbe RMSE en fonction du facteur. Cela permet de montrer clairement comment vous avez choisi le meilleur modèle.
Calcul du volume
dx = mesh["X2"].iloc[0] - mesh["X1"].iloc[0] # largeur d'une cellule
dy = mesh["Y2"].iloc[0] - mesh["Y1"].iloc[0] # hauteur d'une cellule
aire = dx * dy # aire d'une cellule
volume = np.sum(mesh_actif["Epaisseur_m"] * aire) # somme des volumes des cellules
print(volume) # volume total du piege
Références
- Andrés, J., Alcalde, J., Ayarza, P., Saura, E., Marzán, I., Martí, D., Martínez Catalán, J. R., Carbonell, R., Pérez-Estaún, A., García-Lobón, J. L., & Rubio, F. M. (2016). Basement structure of the Hontomín CO2 storage site (Spain) determined by integration of microgravity and 3-D seismic data. Solid Earth, 7(3), 827‑841. https://doi.org/10.5194/se-7-827-2016
- Li, X., & Chouteau, M. (1998). Three-Dimensional Gravity Modeling In All Space. Surveys in Geophysics, 19(4), 339‑368. https://doi.org/10.1023/A:1006554408567